INTRODUCCIÓN
A nivel mundial, la pioderma es una de las enfermedades de la piel más diagnosticada en caninos debido a que su piel posee ciertas características que la hacen propensa a padecer diversos problemas (Ihrke, 1996; Gortel, 2013). Una gran variedad de agentes bacterianos puede aislarse de piodermas en cani nos, entre el l os Staphylococcus spp, Streptococcus spp, Proteus spp, Pseudomonas spp y Escherichia coli (Senturk et al., 2005; Fogel y Manzuc, 2009). Sin embargo, diversos estudios en América Latina demuestran que son mayormente causadas por Staphylococcus spp (Antúnez et al., 2009; Castellanos et al., 2011; Romero, 2014).
Por mucho tiempo se reconoció que dentro de las especies del género Staphylococcus más frecuentes en piodermas caninas se encontraban S. aureus, S. intermedius, S. epidermidis y S. schleiferi (May et al., 2006; Frank et al., 2009). Sin embargo, en 2005, Staphylococcus intermedius, reconocido como el agente involucrado en la mayoría de las piodermas caninas, fue reclasificado en tres especies fenotípicamente similares y agrupados dentro del Grupo de los Staphylococcus intermedius (SIG): S. intermedius, S. pseudintermedius y S. delphini (Devriese et al., 2005; Bannoehr et al., 2007). Posteriormente, Fitzgerald (2009) reportó una mayor frecuencia de S. pseudintermedius involucrado en piodermas caninas y no el S. intermedius, como se solía creer. Asimismo, Wang et al. (2012) determinó una frecuencia de 92% de S. pseudintermedius de los casos clínicos de pioderma canina por estafilococos en China, mientras que Onuma et al. (2011) halló una frecuencia de 76% de S. pseudintermedius en caninos de Japón.
Bioquímicamente, Sasaki et al. (2007) intentó diferenciar al S. pseudintermedius de las otras especies del SIG, no logrando identificar marcadores fenotípicos. La identificación precisa de S. pseudintermedius se basaba en la secuenciación genética (Bannoehr et al., 2007; Sasaki et al., 2007). Sin embargo, Bannoehr et al. (2009) elaboró un método basado en la reacción en cadena de la polimerasa con análisis del polimorfismo de longitud en los fragmentos de restricción (PCR-RFLP) amplificando el gen pta, logrando así, diferenciar S. pseudintermedius y S. aureus de otras especies del género.
En muchos laboratorios, los hallazgos de Staphylococcus no son identificadas a nivel de especie y los cultivos aislados se consideran solo como Staphylococcus sp. Sin embargo, frente al aumento de las cepas resistentes a meticilina y del papel de reservorio que pueden cumplir los caninos domésticos para infecciones en humanos, la identificación de S. pseudintermedius a partir de muestras de animales resulta cada vez más importante (Ralf y Guaguere, 2008; Harrison et al., 2014; Bierowiec et al., 2016). Por ello, el propósito del presente estudio fue detectar S. pseudintermedius en piodermas caninas de muestras aisladas en 2016-2018 en el Laboratorio de Bacteriología de la Facultad de Medicina Veterinaria (FMV) de la Universidad Nacional Mayor de San Marcos (UNMSM).
MATERIALES Y MÉTODOS
Material Experimental
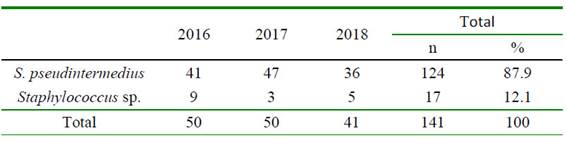
Se tomaron todos los aislados criopreservados de Staphylococcus sp (n=141) provenientes de hisopados de lesiones compatibles con piodermas en perros durante los años 2016 al 2018 que fueron remitidos al Laboratorio de Bacteriología de la FMV-UNMSM, Lima, Perú. Estos aislados criopreservados habían sido identificados como Staphylococcus sp con base a las características fenotípicas de las colonias aisladas y a pruebas bioquímicas convencionales.
Reactivación de Aislados y Extracción de ADN
Los aislados se reactivaron en caldo Tripticasa de soya (TSB) y posteriormente fueron sembrados en agar sangre. La extracción de ADN genómico se realizó con el kit de extracción de ADN GeneJET(tm) Genomic DNA Purification Kit (Thermo Scientific(r)) de acuerdo con las instrucciones del fabricante. Una vez extraído el ADN, se cuantificó y preservó a -20 °C.
Identificación Molecular por PCR-RFLP
Para la estandarización del procedimiento se tomó como referencia el protocolo y los cebadores empleados por Bannoehr et al. (2009) (Cuadro 1).
Se amplificó todas las muestras con las siguientes condiciones: en un volumen de 30 µl con una concentración de 0.2 µM de cada cebador y 15 µl de 2X PCR HotStart MasterMix ABM(r) y 2 µl ADN (30-70 ng/µl). Las condiciones del termociclado incluyeron una desnaturalización inicial a 95 ºC durante 2 min, seguido por 30 ciclos de 95 °C de desnaturalización durante 1 min, 53 °C de hibridación durante 1 min y 72 °C para la elongación durante 1 min, con una elongación final de 72 °C durante 7 min. Por último, 5 µl de cada producto de PCR fue sometido a la digestión con la enzima MboI (5U) en su respectivo buffer 10X y se incubó durante 2 h a 37 °C. Para la corrida electroforética, se preparó el gel de agarosa al 2% con buffer TBE al 0.5X durante 90 min a 80 v. Los productos fueron analizados en el transiluminador SafeVIEW de luz azul.
Validación de los Productos
Se enviaron dos productos para su secuenciamiento a Macrogen Inc (Corea del Sur) para la validación de los productos. Estos productos fueron muestras que amplificaron el gen pta, y además a la digestión con la enzima MboI dando como resultado un producto de 213 bp y 107 bp.
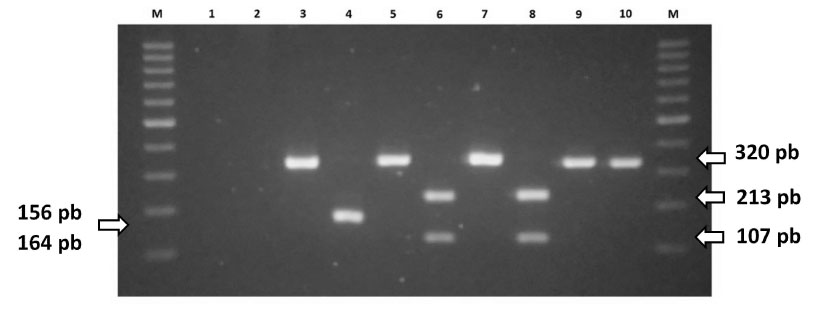
Figura 1 Gel de electroforesis de los productos de pta digeridos con la enzima MboI. M: Marcador molecular 100 bp. Línea 1: Blanco de reacción. Línea 2: Control Negativo E. coli ATCC 8739. Línea 3: Control Positivo Staphylococcus aureus ST 18. Línea 4: Control Positivo Staphylococcus aureus ST18 con digestión MboI. Línea 5: Staphylococcus pseudintermedius S29. Línea 6: Staphylococcus pseudintermedius S29, con digestión MboI. Línea 7: Staphylococcus pseudintermedius S60. Línea 8: Staphylococcus pseudintermedius S60, con digestión MboI. Línea 9: Staphylococcus sp. ST 19. Línea 10: Staphylococcus sp. ST19 con digestión MboI
RESULTADOS
Todos los aislados (n=141) amplificaron la secuencia del gen pta de 320 pb, lo cual los identifica como perteneciente al género Staphylococcus. Posterior a la digestión con la enzima de restricción MboI (PCR-RFLP) al total de aislados de Staphylococcus sp se encontró que 87.9% (124/141) de los aislados poseen el sitio de restricción MboI, dando como resultado un producto de 213 pb y otro 107 pb, que los identifica como S. pseudintermedius (Figura 1).
Por otro lado, no se encontraron aislados que amplifiquen el gen pta y que, al ser sometidos a la digestión con la enzima MboI, corten la secuencia en un lugar diferente, resultando en bandas de 156 pb y otra de 164 pb, lo cual los identificaría como Staphylococcus aureus. Por último, 12.1% (17/141) de los aislados solo amplificó el gen pta sin ser digeridas de allí que no hubo fragmentación de la secuencia, manteniéndose como una sola banda de 320 pb, por lo cual se les consideró como pertenecientes a otras especies dentro del género Staphylococcus (Figura 1, Cuadro 2).
El amplicón del gen pta de los aislados S29 y S60, fueron remitidos a Macrogen Inc. para su secuenciamiento. Las secuencias obtenidas fueron analizadas con los programas ChromasPro, BLASTN 2.9.0 y MegAlign Pro. Luego del alineamiento con otras secuencias del mismo gen disponibles en el banco de genes del National Center for Biotechnology Information (NCBI), mostraron 99.7% de identidad con el gen pta de la cepa S. pseudintermedius HKU10-03 (NC_014925.1) (Figura 2) y con otras cepas obtuvo 99% de identidad (KJ14608.1 y AM945758.1). Las secuencias amplificadas del gen pta de los aislados S29 y S60 fueron ingresadas al banco de genes del NCBI con números de accesión MN480439 y MN480440.
DISCUSIÓN
Los resultados utilizando el protocolo de detección genética de especies de Staphylococcus mediante PCR-RFLP usado por Bannoehr et al. (2009) son reproducibles, los cuales se corroboran con los controles utilizados y el análisis de secuencias del gen pta números de accesión MN480439 y MN480440, de aislados representativos.
Se determinó que el 87.9% de los aislados pertenecen a S. pseudintermedius y 12.1% se identificó como otra especie de Staphylococcus. En cuanto a S. pseudintermedius, los resultados muestran ser similares a otros estudios. Así, Wang et al. (2012) en China registra una frecuencia de 92% de S. pseudintermedius de los casos clínicos de pioderma canina por estafilococos, Bourguignon et al. (2016) en Brasil reportó 93.3% de S. pseudintermedius en piodermas caninas estafilocócicas y Onuma et al. (2011) halló una frecuencia de 76% de S. pseudintermedius en caninos de Japón, este último valor moderadamente inferior a los obtenidos en el presente estudio.
En general, incluyendo el presente estudio, se reportan altas frecuencias de aislamiento de S. pseudintermedius a partir de hisopados de piodermas en caninos. Estos resultados se explican debido a que S. pseudintermedius, al ser el mayor colonizador de la piel de los caninos, es más probable que actúe y esté involucrado como patógeno oportunista ante la alteración de la microbiota de la piel (Rubin y Chirino-Trejo, 2011). Esta situación puede ser más frecuente aun en perros con dermatitis atópica, en quienes se ha reportado tener una mayor frecuencia de S. pseudintermedius como parte de su microbiota (Fazakerley et al., 2009).
Por otro lado, a pesar de que el protocolo de PCR-RFLP, con los cebadores usados poseen la capacidad de identificar a S. aureus, no se obtuvo ningún asilado positivo a partir de piodermas caninas. Sin embargo, no se debe descartar a S. aureus como patógeno en caninos y su potencial rol como reservorio para reinfecciones en humanos (Harrison et al., 2014; Bierowiec et al., 2016).
Finalmente, este estudio constituye el primer reporte de detección molecular de S. pseudintermedius a partir de piodermas caninas en Perú. Estos resultados permitirán realizar estudios de sensibilidad antimicrobiana in vitro o detección de genes involucrados en resistencia antibióticos en estos microrganismos de importancia clínica (Bond y Loeffler, 2012).











 uBio
uBio