INTRODUCCIÓN
El agente causal del síndrome de hepatitis-hidropericardio (HHS) en aves de corral es adenovirus aviar serotipo 4 (FAdV-4) (Mazaheri et al., 1998; Toro et al., 1999; Hess, 2000; Dahiya et al., 2002). La patología es también llamada «enfermedad de Angara», fue reportada por primera vez en Angara, Pakistán (Khawaja et al., 1988). El virus es un miembro de la familia Adenoviridae, género Aviadenovirus y especie Fowl Adenovirus C (Li et al., 2016). La enfermedad afecta el hígado, pericardio y riñones (Anjum et al., 1989; Afzal et al., 1991; Asthana et al., 2013).
La transmisión horizontal del virus ocurre cuando las heces contaminadas se diseminan a través del ambiente del galpón, dando lugar a la infección vía oral-fecal-oral, ocasionando más del 30% de mortalidad en pollos de engorde con 3 a 5 semanas de vida (Pereira et al., 2015). Los FAdV pueden transmitirse verticalmente a través de huevos embrionados, reactivándose el virus en las primeras semanas de vida de los pollitos, especialmente si las aves están inmunosuprimidas (Fadley et al., 1980; Toro et al., 2001; Grgiæ et al., 2006).
Debido a su rápida propagación, es necesario llevar a cabo un monitoreo y control. Para ello se han venido usando pruebas serológicas como la técnica de ELISA (Pan et al., 2020) y la prueba de inhibición de la hemaglutinación (Piela et al., 1983); sin embargo estas pruebas no detectan la especie patógena específica y dan resultados falsos positivos. Con la ayuda de la técnica de PCR (gold standard) como prueba confirmativa se obtiene una alta sensibilidad y mayor especificidad, resultando en un mejor diagnóstico de la enfermedad (Asthana et al., 2013). En el Perú se ha demostrado que las enfermedades por adenovirus aviar son en su mayoría causadas por FAdV-4, siendo también frecuente en Chile y Ecuador, llegando hasta más de 90% de los casos reportados (Rodriguez et al., 2014). Ante esto, el estudio tuvo como objetivo el desarrollo de una técnica de PCR para la detección FAdV-4 en muestras de cultivo celular-células EB66 (células madre de embrión de pato).
MATERIALES Y MÉTODOS
Cepa Viral y Cultivo Celular
La cepa de virus adenovirus aviar 4 (FAdV-4) forma parte del cepario del Laboratorio de Farvet (Ica, Perú), la cual fue incubada en cultivo de células EB66 (células madre de embrión de pato) en suspensión. Se utilizó el medio CD Hybrydoma suplementado o medio ExCell EBX GRO I suplementado (Sigma) durante 48 horas a 37 °C con 5% de CO . Una vez que el cultivo obtuvo una concentración de 6 x 106 células/ml se le infectó con FAdV-4 a una multiplicidad óptima de infección (M.O.I) de 0.02. El cultivo infectado se incubó a 37 °C con 5% de CO durante de 6 días, para luego extraer 500 ml para su distribución en tubos Falcon® de 15 ml.
Cebadores
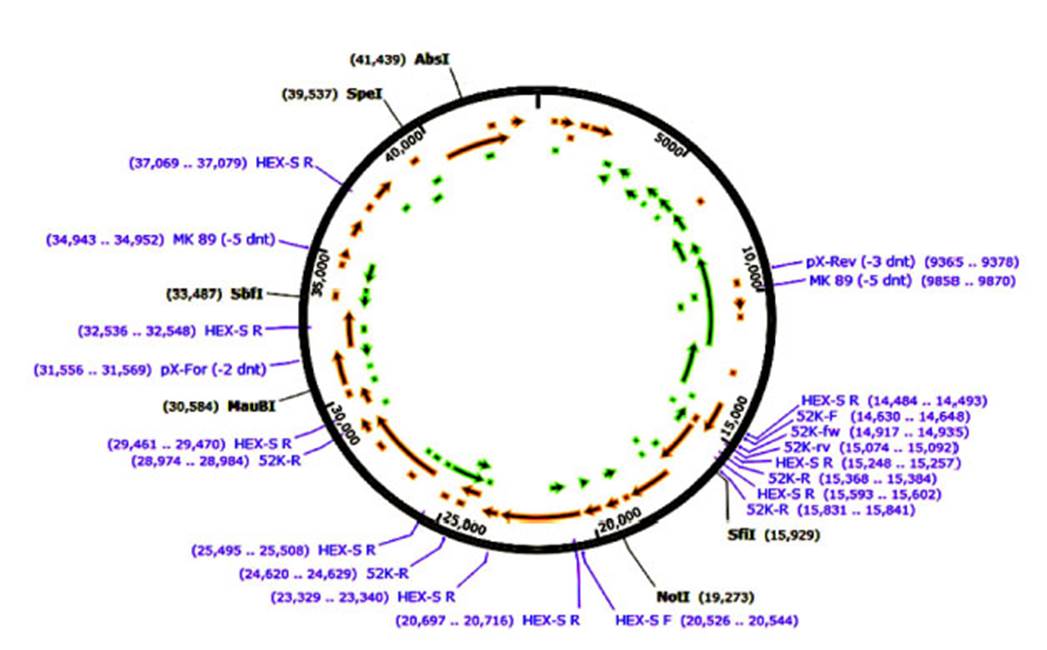
Se seleccionaron los cebadores candidatos dirigidos a las regiones del genoma de FAdV-4 (Figura 1) (Xie et al., 1999; Romanova et al., 2009; Steer et al., 2009; Günes et al., 2012) a través del programa bioinformático SnapGene Viewer v. 3.3.3 (GSL Biotech, USA). Los cebadores fueron sintetizados de forma (IDT, USA). Las secuencias de los cebadores se presentan en el Cuadro 1. Para facilitar su identificación se utilizaron nombres internos.
Purificación de FAdV-4 y Material de Referencia Interna (M.R.I)
Para su purificación se utilizó el polietilenglicol (PEG) siguiendo las especificaciones del fabricante (Abcam, USA). Dicha metodología consistió en centrifugar las células infectadas a 3200 x g por 15 min a 4 °C, para luego colectar el sobrenadante y agregar 2.5 ml de PEG por cada 10 ml de sobrenadante obtenido. La mezcla se incuba durante la noche a 4 °C, para luego centrifugarla a 3200 x g durante 30 min a 4°C. El sobrenadante se extrae y el pellet viral obtenido por tubo se resuspende en 1.5 ml de buffer fosfato salino estéril 1X y el virus resuspendido se alícuota en porciones de 500 µl en tubos de 2 ml.
De estas alícuotas se tomaron 200 µl para extraer el ADN del virus utilizando el QIAamp MinElute Virus Spin Kit, (QIAGEN) siguiendo las especificaciones del fabricante.
El ácido nucleico viral fue eluido en 60µl de buffer AVE. Se cuantificó el ADN viral con el equipo Fluorómetro Qubit 2.0 (Life Technologies, USA), siguiendo las indicacio nes del fabricante. Esta metodología tiene la ventaja de presentar una alta sensibilidad analítica, alto rendimiento y una mayor tolerancia a los contaminantes (Sah et al., 2013). Se calculó el grado de pureza por espectrofotometría usando el BioPhotometer (Eppendorf), verificando que el ratio entre las absorbancias se encuentre entre 260 nm/280 nm (Warburg et al., 1942). Así mismo el resultado obtenido por el método de fluorometría y el dato del tamaño total del genoma de MG (Papazisi et al. 2003), sirvieron para calcular el número de copias virales teóricas (Whelan et al., 2003). A este ADN viral obtenido y cuantificado se le denominó material de referencia interno (M.R.I.), el cual se almacenó en alícuotas de 7 µl en tubos de PCR a -80 °C.
Cuadro 1 Características de los cebadores dirigidos a las regiones del genoma de FAdV4

HHS: Síndrome de hidropericardio-hepatitis
1 Temperatura del fabricante; 2: Temperatura calculada
Optimización de la PCR Convencional
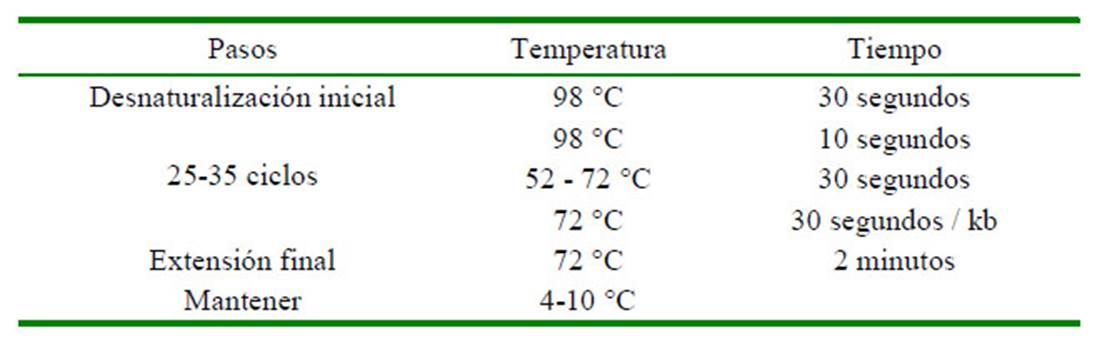
Una vez obtenido el M.R.I. se procedió a bajar la molaridad a cada cebador desde una concentración de 100 µmol/l (liofilizada) hasta 10 µmol/l, usando el buffer TE 1X a un pH 8.0. Una vez obtenido la concentración de 10 µmol/l de los sets de cebadores, se procedió a preparar el Mix siguiendo las especificaciones del inserto del kit de PCR Q5® High-Fidelity 2X Master Mix. Para la programación de la PCR se usó el termociclador Mastercycler proS (Eppendorf). La programación se hizo en base al Protocolo Q5® High-Fidelity 2X Master Mix (Cuadro 2).
Prueba de Gradiente de Temperatura
Luego de preparar el Master Mix se procedió a diluirlo en tubos de PCR. Se colocaron en la placa (de izquierda a derecha columna 01 a columna 12) del termociclador Mastercycler proS, con un rango de temperatura de hibridación entre 52 y 72 °C (Cuadro 3). Este procedimiento se hizo para cada cebador adquirido correspondiente a cada cepa bacteriana de estudio con el fin de saber la temperatura en que se visualizan las dos por medio de una electroforesis en gel de agarosa al 2% con una carga eléctrica de 80 v durante 65 min a fin de determinar la con bandas de los amplicones mediante la electroforesis.
Prueba de Concentración de Cebadores
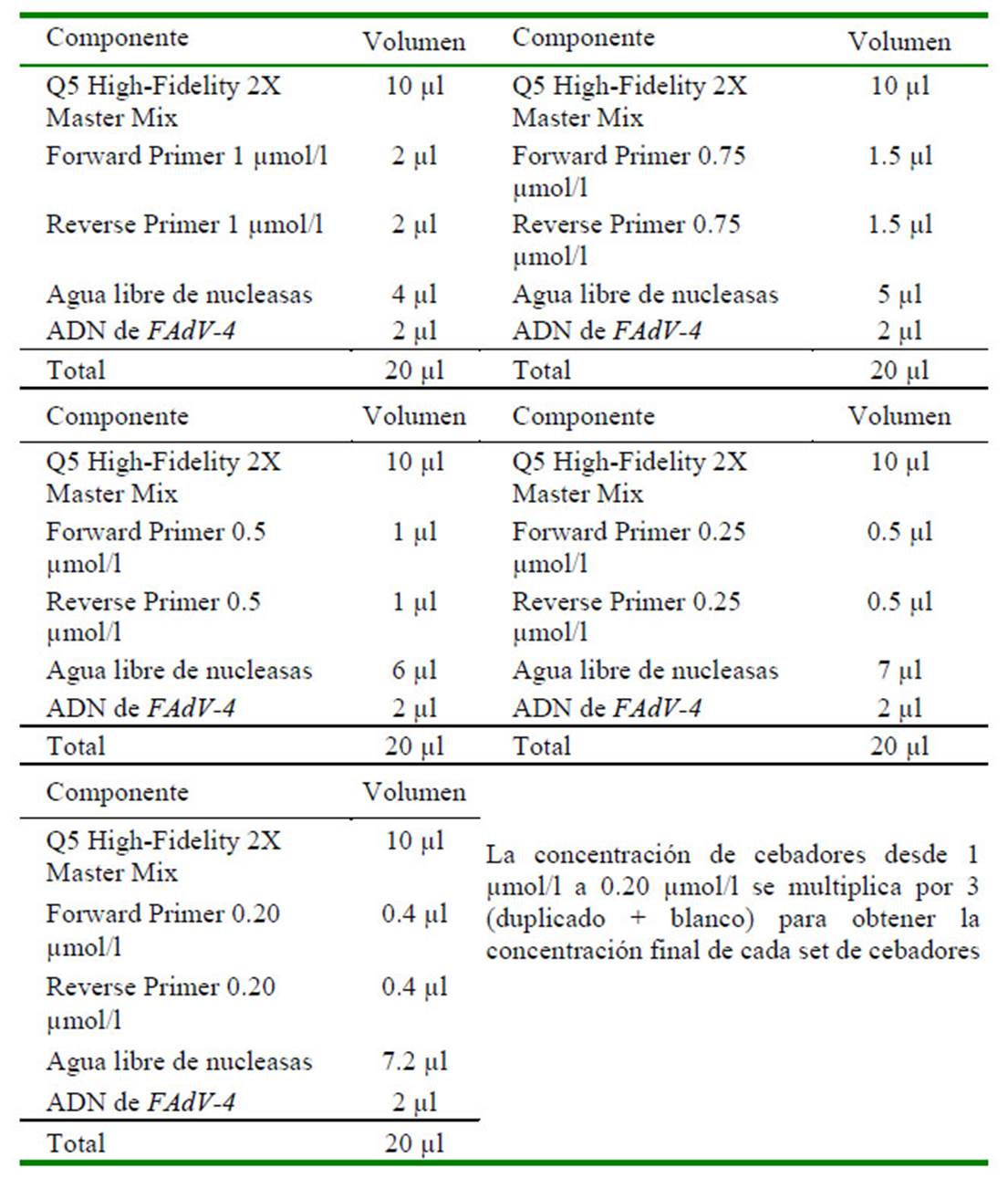
Una vez demostrado las temperaturas óptimas para la expresión de las bandas de los amplicones para cada juego de cebadores, se procedió a preparar el Master Mix a diferentes concentraciones, partiendo desde 1 µM hasta 0.20 µM (Cuadro 4). Se eligió la menor concentración de los cebadores que expresan bandas de los amplicones al ser evalua-
Prueba de Sensibilidad
Esta prueba consistió en realizar 10 diluciones logarítmicas seriadas de suspensión viral (Cuadro 5) con el fin de saber el límite de detección de los amplicones de ADN mediante una electroforesis en gel de agarosa al 2%. Este procedimiento se hizo para cada cebador seleccionado, siempre y cuando hayan pasado la prueba anterior. Se seleccionaron a los cebadores que presentan bandas de amplicones específicas con un mayor número de diluciones.
Prueba de Especificidad
Esta prueba permite determinar si los cebadores seleccionados son únicamente válidos para detectar FAdV-4. Para ello se utilizaron muestras positivas para diferentes virus y bacterias aviares: virus de la enfermedad de Newcastle (NDV), virus de la bronquitis infecciosa (IBV), virus de laringotraqueítis infecciosa (ILTV), metapneumovirus aviar (AMPV), virus de la enfermedad de bursitis infecciosa (IBDV), virus de la anemia aviar (CAV), síndrome de caída de la postura (EDS), ADN puro de células de fibroblasto de pollo (DF1), Pasteurella spp, Salmonella gallinarum, Mycoplasma spp y agua como blanco. Los amplicones de ADN se visualizaron mediante una electroforesis en gel de agarosa al 2%. Se seleccionó el cebador específico para la detección de FAdV-4.
Para determinar la sensibilidad y especificidad de cada set de cebadores (HHS*-2, HHS*-3 y HHS*-4) se procedió según lo indicado en el Cuadro 6. De esta manera se determinó la proporción de muestras correctamente diagnosticadas con el virus de interés por la prueba diagnóstica en estudio (PCR).
RESULTADOS
La cantidad promedio de amplicón del ADN extraído fue de 46.3 µg/µl. El ratio de la muestra de ADN fue de 1.91 teniendo 60% de ácido nucleico y 40% de proteínas. El número de copias virales fue de 9.662 x 107.
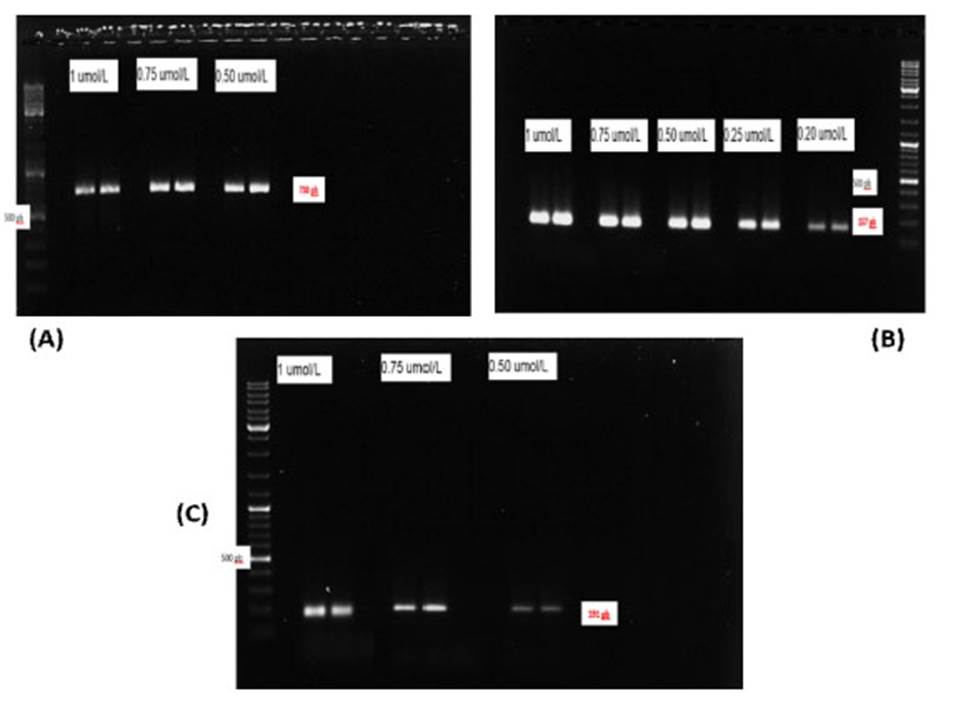
En la Figura 2 se visualizan las bandas de los amplicones de cada cebador (HHS*-1, HHS*-2, HHS*-3, HHS*-4 y HHS*-5), a una gradiente de temperatura desde 51.8 a 72 °C. Se aprecia que solo los cebadores HHS*-2, HHS*-3, HHS*-4 presentaron bandas específicas para su respectivo tamaño del amplicón, especialmente el cebador HHS*-3, quien presentó bandas específicas en cada rango de temperatura. En la Figura 3 se visualizan las bandas de los amplicones de estos cebadores a diferentes concentraciones (1, 0.75, 0.5, 0.25, y 0.20 µmol/l), destacando el cebador HHS*-3, debido a que las bandas llegan hasta la concentración de 0.20µmol/l.
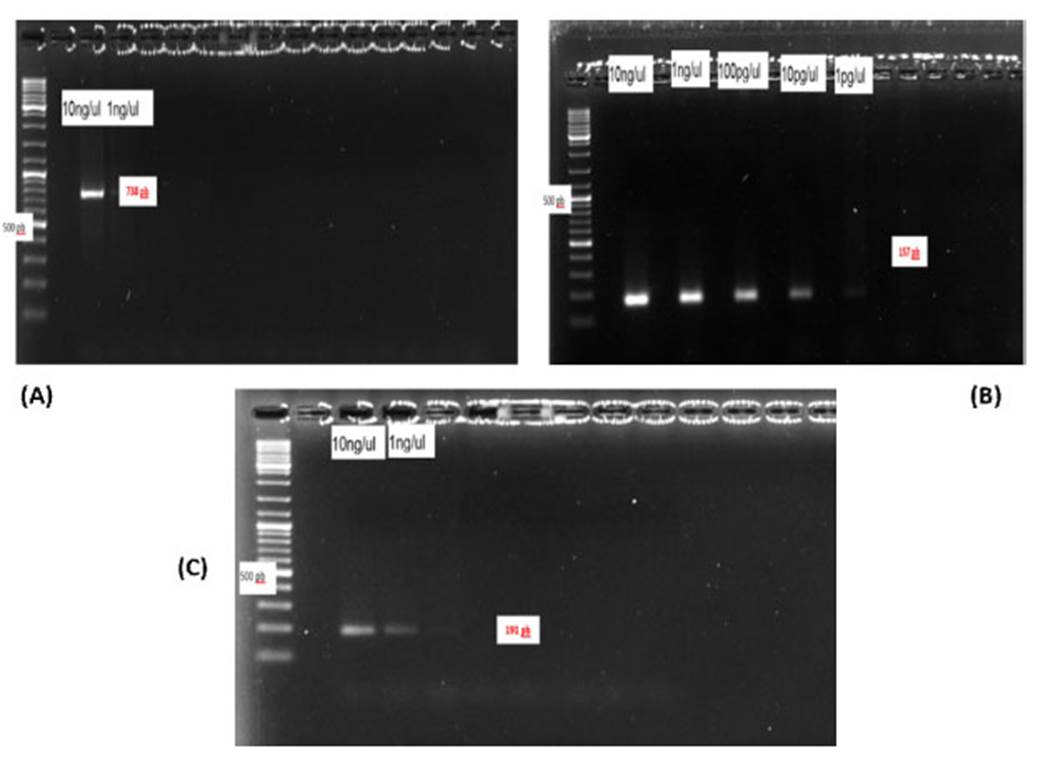
En la Figura 4 se visualizan los amplicones de los cebadores HHS*-2, HHS*-3, HHS*-4, a diferentes concentraciones del amplicón (10 ng/µl, 1 ng/µl, 100 pg/µl, 10 pg/µl y 1 pg/µl), destacando el cebador HHS*-3, debido a que presentaba bandas específicas hasta una concentración de 1 pg/µl del amplicón.
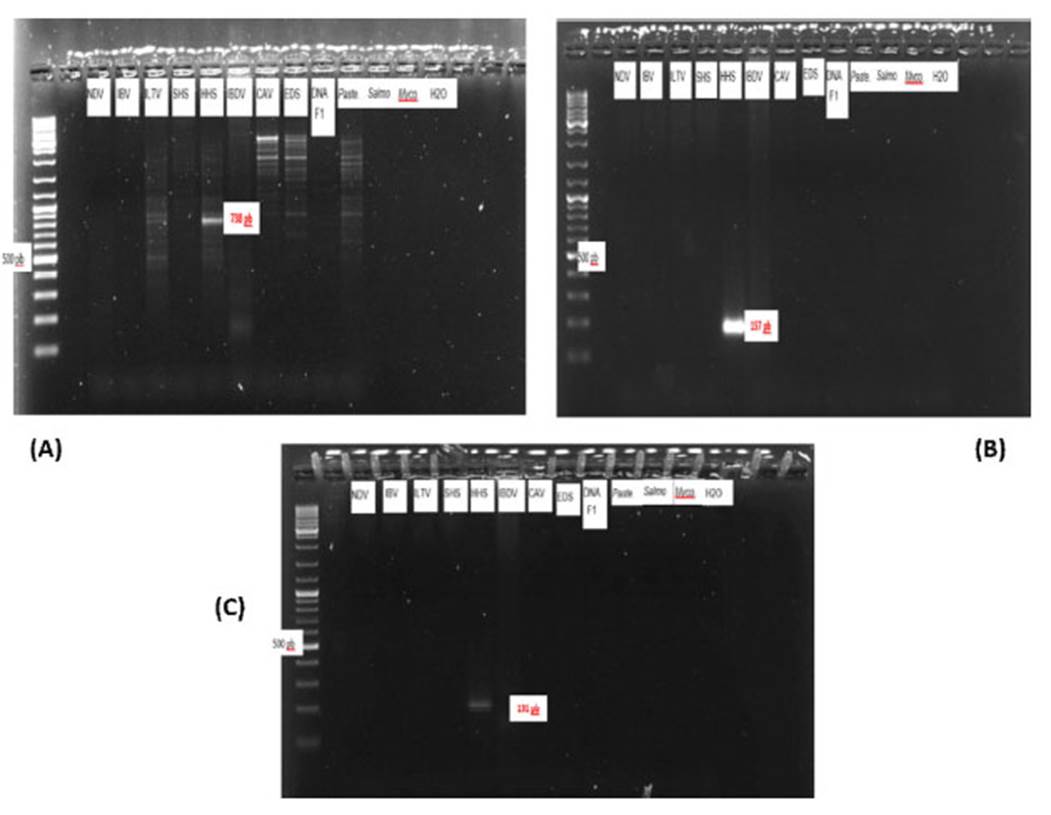
En la Figura 5 se visualizan los amplicones de los cebadores HHS*-2, HHS*-3, HHS*-4 con sus respectivos controles negativos de varios patógenos, incluyendo el HHS y un control blanco. Se visualizaron bandas tenues del cebador HHS*-4, mientras que para el cebador HHS*-3 presentaron bandas resaltantes con especificidad. En el Cuadro 7 se resume la expresión de las bandas del amplicón para cada set de cebadores con estos patógenos.
Los resultados a las pruebas de sensibilidad y especificidad fueron:
HHS*-2: Sensibilidad de 100% y especificidad de 46.15% hasta una concentración del amplicón de >1 ng/µl.
HHS*-3: Sensibilidad y especificidad de 100%, hasta una concentración del amplicón de >1 pg/µl.
HHS*-4: Sensibilidad de 100% y especificidad de 91.67%, hasta una concentración del amplicón de >1 ng/µl.
DISCUSIÓN
Se desarrolló una técnica sensible y específica de PCR para la detección de Fowl adenovirus tipo 4 (FAdV-4) en cultivo de células EB66. Se realizó la búsqueda de referencias bibliográficas para la selección de los cebadores, resultando un total de al menos cinco pares de cebadores para detectar los virus de interés (Xie et al., 1999; Romanova et al., 2009; Steer et al., 2009: Günes et al., 2012).
La detección del adenovirus aviar se logra, en su mayoría, mediante el cultivo celular. El uso del microscopio electrónico ayuda a confirmar la presencia de adenovirus en tejidos (McFerran et al., 2003), pero esta metodología es demandante de tiempo y no permite una adecuada caracterización de los virus con respecto a su clasificación.
Cuadro 6 Principales parámetros para la descripción de la sensibilidad y especificidad
| Resultados prueba | Gold standard | Total | |
| Muestras positivas | Muestras negativas | ||
| Positivos Negativos | A C | B D | Positivos A+B Negativos C+D |
| Total | A+C | B+D | N |
(A) Verdaderos positivos; (C) Falsos negativos; (B) Falsos positivos; (D) Verdaderos negativos; (N) Total
Cuadro 7 Prueba de especificidad para los cebadores utilizando diversos patógenos aviares
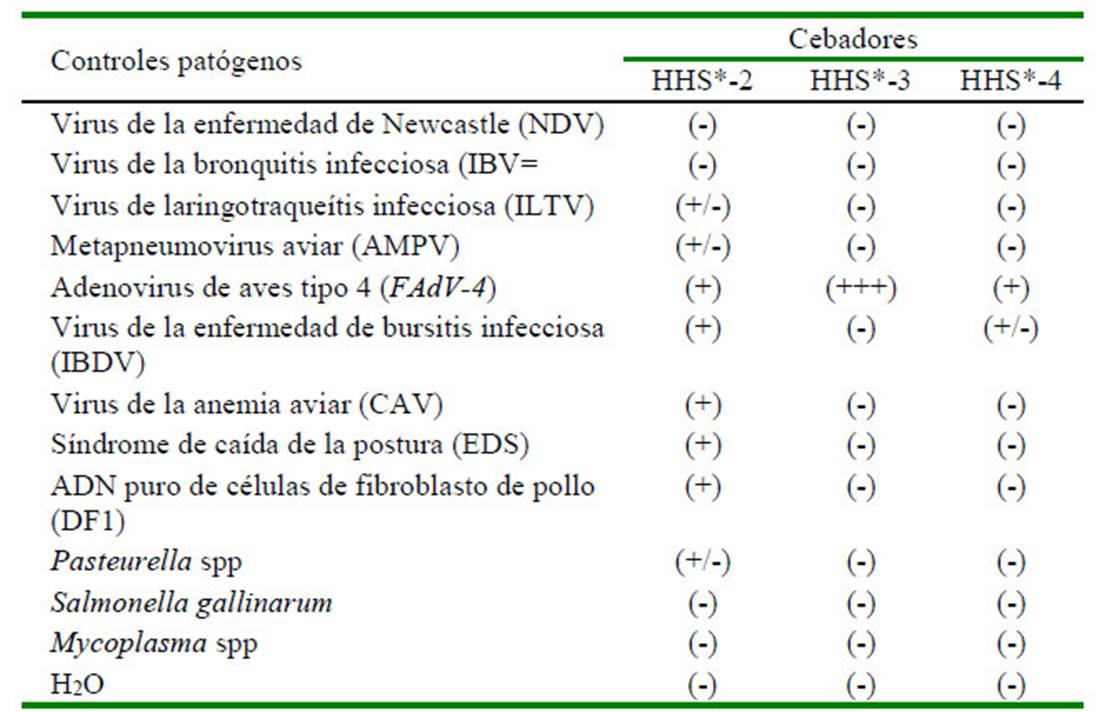
(-) Ausencia de Bandas (+/-) Bandas tenues con inespecificidad; (+) Bandas tenues con especificidad; (+++) Bandas resaltantes con especificidad
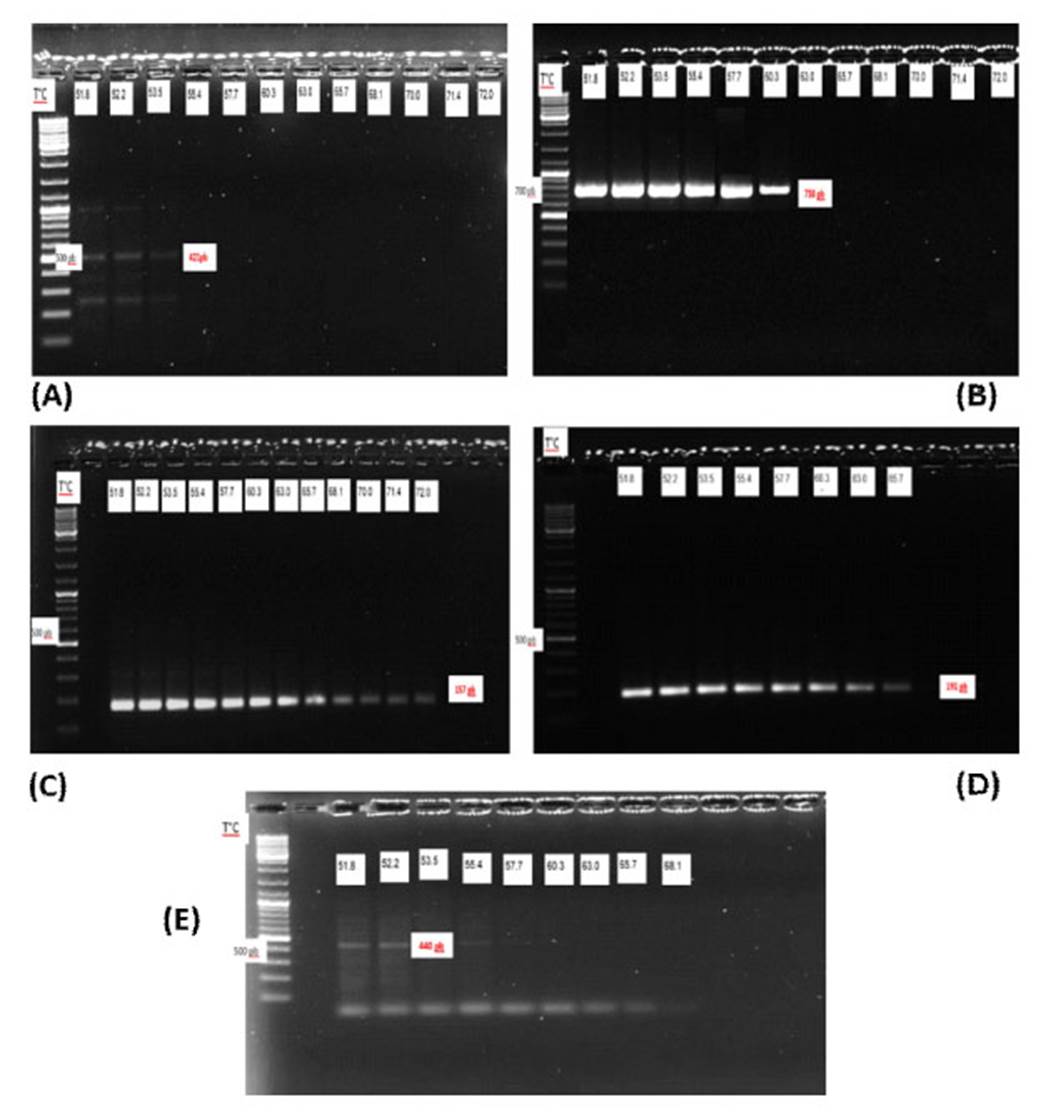
Figura 2 Prueba de gradiente de temperaturas para los cebadores candidatos (A: HHS*-1; B: HHS*-2; C: HHS*-3; D: HHS*-4; E: HHS*-5)
Los cebadores fueron sometidos a diferentes pruebas con la finalidad de escoger el más apropiado para la detección de FAdV-4. En la prueba de gradiente de temperatura (51.8 72 °C) se demostró que la temperatura ideal fue de 60 °C para los cebadores HHS*-2, HHS*-3 y HHS*-4; sin embargo, los cebadores HHS*-1y HHS*-5 presentaban bandas inespecíficas, debido a que estos cebadores presentan secuencias de nucleótidos para detectar la cepa CELOFowl adenovirus1 y la cepa A2-A-Fowl adenovirus 9, respectivamente (Xie et al., 1999; Romanova et al., 2009).
Los cebadores HHS*-2, HHS*-3 y HHS*-4 (Günes et al., 2012) lograron pasar las tres primeras pruebas, pero el cebador HHS*-2 no fue específico debido a que las bandas de los amplicones se visualizaron en otros virus patógenos como laringotraqueitis (ILTV), bursitis infecciosa aviar (IBDV), virus de la anemia aviar (CAV), síndrome de la caída de la postura (EDS) y la bacteria Pasteurella spp, lo cual se debe a que parte de las secuencia de nucleótidos se evidencia en el genoma de los virus y bacteria mencionados
CONCLUSIONES
Se desarrolló una técnica de PCR para la detección de Fowl adenovirus tipo 4 (FAdV-4) en muestras de tejidos.
Los cebadores que se seleccionaron para la detección de FAdV-4 fueron HHS*-2, HHS*-3 y HHS*-4, de los cuales sólo HHS*-3 y HHS*-4 fueron efectivos, destacando HHS*-3, ya que su sensibilidad llegó hasta una concentración del amplicón de e»1 pg/µl y 100% de especificidad












 uBio
uBio