Servicios Personalizados
Revista
Articulo
Indicadores
-
 Citado por SciELO
Citado por SciELO
Links relacionados
-
 Similares en
SciELO
Similares en
SciELO
Compartir
Revista Peruana de Medicina Experimental y Salud Publica
versión impresa ISSN 1726-4634
Rev. perú. med. exp. salud publica v.17 n.1-4 Lima 2000
TRABAJOS ORIGINALES
Tipificación Molecular del Vibrio cholerae O1 en el Perú
José Huguet T1; Isabel Arias B1; Ysabel Montoya P2.
1 Laboratorio de Enteropatógenos, División de Bacteriología, Centro Nacional de Laboratorios en Salud Pública, Instituto Nacional de Salud.
2 División de Biología Molecular, Centro Nacional de Laboratorios en Salud Pública, Instituto Nacional de Salud.
RESUMEN
Este estudio de ribotipificación en 75 cepas de Vibrio cholerae O1 permitió identificar tres variantes ribotípicas, referidas como Per1, Per2 y Per3, aisladas durante el periodo 1991- 1999 en el Perú. La variante Per1 fue reportada tanto en la etapa epidémica y endémica del cólera, mientras que Per2 y Per3 se relacionaron sólo con la etapa endémica. Los resultados mostraron además una aparición constante y mayoritaria de la variante Per1, poniendo en evidencia la emergencia de un mismo grupo clonal en los brotes epidémicos del Perú. Las variantes ribotípicas encontradas fueron comparadas con los ribotipos de diferentes cepas referenciales de V. cholerae previamente caracterizadas. Se observó una identidad total del ribotipo Per1 con la variante ribotípica de aislamientos Asiáticos (Tailandia), encontrándose además altos índices de similitud entre los ribotipos Per1, Per2 y Per3, y evidenciándose una estrecha relación entre las cepas peruanas y los aislamientos asiáticos.
Palabras claves: Vibrio cholerae, Ribotipificación; ARN ribosómico; Perú (fuente: BIREME).
ABSTRACT
Ribotyping of seventy five Vibrio cholerae O1 strains collected from 1991 to 1999, revealed three different ribotypes, referred to as Per1, Per2 and Per3. Per1 ribotype was found in both the endemic and epidemic periods, while Per2 and Per3 ribotypes were found only in the endemic period. The results showed a more frequent and constant presence of ribotype Per1, and indicated the emergence of the same clonal group in the aforementioned outbreaks. At the same time, new ribotypes were compared against ribotypes from previously characterized V. cholera referential strains. The comparative analysis using similar ratios revealed a total coincidence between Per1 ribotype and the ribotype from Thailand isolates, exhibiting high similarity ratios between Per1, Per2 and Per3 ribotypes. This finding supports the close relationship between Peruvian and Asian strains of V. cholerae.
Key words: Vibrio cholerae, Ribotyping; RNA, ribosomal; Peru (source: BIREME).
INTRODUCCION
En 1991, el cólera apareció en forma epidémica en varias ciudades de la costa del Perú. El establecimiento de reservorios para el Vibrio cholerae, favorecido, entre otros factores, por la existencia de malas condiciones higiénico-sanitarias en la población, propiciaron los procesos de recombinación genética entre cepas de V. cholerae, dando origen a la aparición de variantes, que pasarían inadvertidos debido a que no se cuenta con técnicas modernas para su detección.
En la actualidad, los métodos que analizan directamente el ADN o ARN de los organismos han mostrado resultados promisorios en el estudio epidemiológico del cólera1,2,3 . El análisis en longitud de fragmentos de restricción (RFLP), es uno de los métodos más usados en la caracterización de varios microorganismos de importancia médica. La agrupación de bacterias en un sistema de tipificación usando sondas de genes que codifican el ARN ribosomal, se denomina ribotipaje.
El presente trabajo tiene como objetivo describir la variabilidad genética en los aislamientos de V. cholerae ocurridos en el Perú durante la última década. Buscamos, mediante patrones moleculares, caracterizar las cepas de V. cholerae y correlacionar la variabilidad genética encontrada a la curva epidemiológica de enfermedad entre 1991-1999. Asimismo, buscar similitudes genotípicas entre cepas peruanas y aislamientos de otros lugares a nivel mundial, utilizando como referencia en banco de datos para patrones de hibridación, originados a partir del gen codificante del ARN ribosomal 16S3.
MATERIALES Y METODOS
SELECCIÓN DE CEPAS DE Vibrio cholerae O1
Todas las cepas fueron obtenidas del cepario del Laboratorio Referencial de Enteropatógenos del Instituto Nacional de Salud.
Tomando en cuenta la naturaleza descriptiva del trabajo, se consideraron como puntos de referencia 11 departamentos del territorio peruano que reportaron casos de cólera entre el periodo 1991-1999. Los puntos de referencia fueron: Lima, La Libertad, Piura, Huancayo, Junín, Ayacucho, Puno, Ancash, Cusco, Cajamarca e lquitos. Luego, el proceso de selección de cepas fue realizado en forma aleatoria tomando en cuenta los brotes epidémicos reportados en cada año de estudio. Las cepas fueron reactivadas en caldo alcalino peptonado y TCBS agar. Se excluyeron aquellas cepas que no presentaban información completa y detallada de la fecha y lugar de aislamiento, serogrupo y biotipo. A partir de estos procedimientos se seleccionaron un total de 75 cepas de Víbrio cholerae O1.
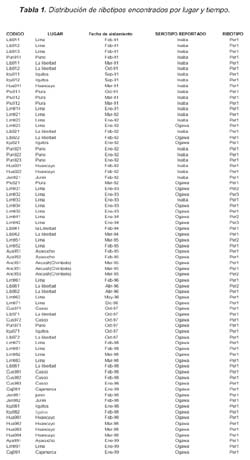
Cada cepa fue codificada con las tres primeras letras del lugar de procedencia, seguidas del año de aislamiento y un número de orden respectivo (Tabla 1).
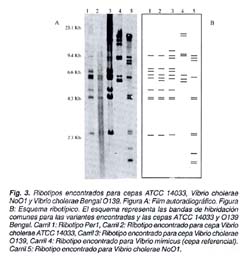
Las cepas de referencia utilizadas fueron: Cepa Vibrio cholerae O1 ATCC14033. Biotipo El Tor, serotipo Inaba; Víbrio cholerae O139 Bengal tipificada y Cepa Vibrio cholerae NoOl tipificada y una cepa de Vibrio mimicus. Asimismo, se utilizaron esquemas ribotípicos anteriormente reportados para realizar las comparaciones respectivas3.
PROCEDIMIENTOS
Extracción de ADN genómico
Para la extracción de ADN genómico se utilizó el método fenol/cloformo4. Primero, se centrifugó 5 mL de suspensión bacteriana y el sedimento fue resuspendido en solución de lisis conteniendo lisozima; posteriormente, se adicionó lauril sulfato de sodio (SDS) y proteinasa K llevando a 65°C durante 2 horas. EL ADN fue extraído con fenol/cloroformo, precipitado con etanol y resupendido en agua tridestilada.
Ribotipificación
El ADN obtenido de cada de V. cholerae fue ribotipificado mediante el método descrito por Popovic3 ,digiriendo 8 μg de ADN con 5 U de enzima BglI durante 2 horas. Posteriormente, los productos de restricción fueron sometidos a electroforesis en un gel de agarosa al 1% y transferidos a una membrana de nylon mediante el método de Southern blot5. Los productos de digestión fijados en la membrana fueron hibridados con una sonda de ~1480 bp, correspondiente al gen codificante del ARN ribosomal 16S (ADNr 16S) (Figura 1). El método utilizado fue el método quimioluminiscente6 . La sonda del gen ADNr 16S fue obtenida mediante reacción en cadena de la polimerasa (PCR), a partir de ADN de V. cholerae, utilizando iniciadores universales para su amplificación7 . Estos iniciadores utilizados fueron: RIBF' AGAGTTGATMTGG3 y RIBR5 TACCTTGTTACGACTT3; y el protocolo para la reacción en cadena de la polimerasa fue: denaturación inicial 95°C por 5 minutos, luego 30 veces el siguiente ciclo: 95°C por 30 segundos, 33°C por 1,5 minutos y 72°C por 2 min. Finalmente se realizó una extensión final a 72°C por 10 minutos. Toda la reacción se llevo a cabo en un termociclador Genamp 2400.
El proceso de hibridación con la sonda y los productos de restricción se llevó a cabo a 42°C durante 4 horas. Finalmente, la detección de la hibridación se reveló por autoradiografía4 , observándose un patrón de bandas para cada cepa de V. cholerae. Cada variante obtenida por ribotipificación (ribotipo) fue rotulada con las iniciales Per, seguida del código respectivo que identificaba la fecha y lugar de aislamiento.
Cálculo de cladogramas
Los perfiles de hibridación obtenidos en el film fueron esquematizados, alineando cada banda y tomando como referencia los pesos moleculares del marcador λHindlll. Todas las cepas ribotipadas fueron esquematizadas y comparadas con las cepas ATCC14033, BengalO139 y V. cholerae NoOl. Las comparaciones con aislamientos a nivel mundial fueron realizadas utilizando como referencia los esquemas de ribotipos reportados, en los cuales se incluía una cepa V. cholerae Perú 19913.
Los índices de similitud para el cálculo de cladogramas fueron obtenidos usando la relación:
Los cladogramas fueron diseñados ordenando los índices de similitud por cada patrón ribotípico en una tabla de doble entrada, utilizando como interfase el editor de textos NOTEPAD (Windows 97) y archivándolo en formato TXT. El archivo TXT fue evaluado con el algoritmo "Método de emparejamiento por pares usando promedios aritméticos" (UPGMA-Unweighted pair group method using arithmetic average)9.
RESULTADOS
Tres perfiles ribotípicos distintos fueron observados en las 75 cepas evaluadas. El perfil ribotípico predominante en las cepas de V. cholerae fue Per1, alcanzando 92% del total de cepas seleccionadas y apareciendo en todos los años con la mayor frecuencia. Los ribotipos restantes (Per2, Per3) se presentaron en menor número y estuvieron relacionados a los años 1993, 1994, 1995 y 1996, apareciendo tanto en aislamientos de Lima como del norte del País (Tabla 1).
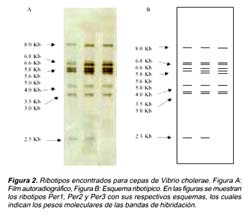
El ribotipo Per1 mostró un patrón de nueve bandas definidas (8,0; 6,8; 6,6; 5,8; 5,6; 4,0; 3,5; 3,0 y 2,3 Kb), el ribotipo Per2 mostró un patrón de 10 bandas definidas (8,0; 6,8; 6,6; 5,8; 5,6; 5,0; 4,0; 3,5; 3,0 y 2,3 Kb), y el ribotipo Per3 mostró un patrón de 9 bandas definidas (8,0; 6,8; 6,6; 5,8; 5,6; 5,0; 4,0; 3,5 y 3,0 Kb) (Figura 2).
Para la cepa ATCC 14033 se obtuvo un patrón de RFLP similar al ribotipo Per1, con la diferencia en la ausencia de la banda de 6,6 Kb y la presencia de la banda de 5,0 kb. Para la cepa O139 Bengal se obtuvo un patrón de bandas similar a la variante Per1, con la adición de dos bandas de 12 y 7,5 Kb. Para la cepa NoOl se obtuvo un patrón distinto a las cepas anteriormente evaluadas, con solo tres bandas en común de 8,0; 3 y 2,3 Kb. con las variantes Per1 y Per2. No se encontró similaridad en ninguno de los casos con la cepa de Vibrio mimicus. (Figura 2 y 3).
Partiendo del análisis de patrones numéricos y obteniendo los índices de similitud, se calculó el cladograma, el cual graficaba la similitud entre los ribotipos obtenidos y las cepas referenciales de V. cholerae (ATCC14033, NoOl y O139 Bengal). Los resultados agruparon a los ribotipos obtenidos junto con las cepas de V. cholerae ATCC 14033 y también con la cepa 0139 Bengal, dejando en una rama distante a la cepa de V. cholerae NoOl . Los ribotipos Per2 y Per3 fueron subagrupados en una rama, relacionándose en similitud con el ribotipo Per1 y la cepa referencial ATCC 14033 (Figura 4).
Un segundo cladograma mostró dos grupos bien diferenciados (Grupo Clásico y Grupo El Tor). El grupo denominado Clásico involucró aislamientos de brotes en India 1960, 1949, 1941, 1940, y Bangladesh 1960 y 1972. En tanto que el grupo denominado El Tor involucró a cepas relacionadas con la séptima pandemia, en las que se destacó las cepas aisladas en brotes peruanos.
Los análisis de los ribopatrones indicaron una identidad total del ribotipo Per1 con el ribotipo de los aislamientos Perú 1991 y Tailandia 1991, estudiados por Popovic3.
Dentro del grupo el Tor se pudo establecer subgrupos, en los cuales se relacionó a los tres ribotipos encontrados en el presente estudio. Estos tres ribotipos se encontraron en un mismo clado junto con aislamientos de Filipinas y Ruanda, indicando además una alta similitud con los aislamientos asiáticos (1992) y con Islas del Pacifico Sur- Islas Gilbert- Oceanía (1977). Otros aislamientos relacionados a las variantes peruanas fueron California (1991), Hawai (1991), Rumania (1991) y una cepa aislada de un brote en Guatemala, en 1990 (Figura 5).
DISCUSION
Revisando la distribución de los ribotipos encontrados destaca la aparición constante de Per1 en todos los lugares estudiados, evidenciándose su distribución uniforme y mayor frecuencia. Los dos restantes ribotipos Per2 y Per3, aparecieron también en diferentes lugares del Perú, aunque con una menor frecuencia de presentación.
La presencia de un ribotipo dominante Per1 reportado en el presente trabajo, reafirma el momento endémico del cólera en el Perú. Trabajos anteriores también publican la presencia constante de este ribotipo Per13,11, reforzando la teoría que en cada brote epidémico ocurrido en Latinoamérica reemerge la misma variante genética de V. cholerae.
En cuanto a la distribución cronológica, Per1 mantiene una frecuencia alta, estando relacionada con el inicio de la epidemia en el Perú y los últimos brotes reportados en 1999; en tanto que las variantes encontradas Per2 y Per3 fueron aisladas en los años 1993, 1994, 1995 y 1996, y se correlacionan con el descenso de la curva epidémica y emergen a comienzos de una etapa endémica en el Perú.
Utilizando relaciones basadas en índices de similitud se corrobora a la epidemia latinoamericana del cólera como una extensión de la séptima pandemia, agrupándose a los ribotipos encontrados en un grupo homogéneo derivado de cepas asiáticas, ya descritas con anterioridad por otros autores3.
Los resultados obtenidos al agrupar los patrones de referencia en el ámbito mundial con los ribotipos obtenidos en el presente trabajo coinciden con la agrupación fenotípica de Vibrios en lo que respecta al biotipo. Todas las variantes de V. cholerae pertenecientes al biotipo Clásico se agrupan en una rama mayor, mientras que las variantes pertenecientes al grupo El Tor pertenecen a un grupo homogéneo, como se describió anteriormente. Adicionalmente, se presenta una subagrupación en las variantes del grupo El Tor, encontrándose posibles relaciones entre epidemias provocadas por la misma cepa (Perl/Tha91)3,12 , brotes aislados (Guate90)3 o variantes provenientes de reservorios o zonas endémicas de cólera (Austral77, Austral84)3 . Esta correlación demuestra la eficacia del método de ribotipaje cuando se utiliza un banco de variantes como referencia y se compara con nuevo ribotipos encontrados. Ello debido a la excelente repetitividad de la prueba y su aceptable discriminación.
El análisis entre ribotipos encontrados en cepas peruanas y cepas de referencia Bengal y NoOl indican una alta similitud entre la cepa O139 con el grupo al que pertenecen las cepas peruanas, encontrándose más alejado el grupo de las cepas NoOl. Este hecho corrobora los resultados obtenidos por otros autores, respecto a la relación entre cepas toxigénicas O1 de V. cholerae y la cepa responsable de epidemias en Asia O139 – Bengal 10,11.
Se reconoce variabilidad en las poblaciones de V. cholerae O1 en el Perú, encontrándose tres variantes ribotípicas muy similares entre sí y relacionadas con aislamientos asiáticos de la séptima pandemia del cólera. Sin embargo, cabe mencionar que la variante Per1 se encuentra relacionada a la mayoría de brotes epidémicos de cólera en el país, lo cual también es corroborado por un estudio realizado en la ciudad de Lima en el periodo 1991-199511.
En la actualidad se están empleando nuevas metodologías que permiten una mayor discriminación entre cepas bacterianas. La electroforesis en campo pulsado es una de las técnicas que ha cobrado una mayor importancia en la tipificación de bacterias11 y otras, como el polimorfismo en longitud de fragmentos amplificados (AFLP- Amplified- fragment length polymorphism)12 también está siendo cada día mas usada. Sin embargo, la ribotipifcación no deja de ser una herramienta de suma importancia para el estudio en la variabilidad y epidemiología del cólera y otras enfermedades transmisibles, repotenciando las metodologías convencionales para el estudio de epidemias.
Finalmente, teniendo en cuenta las comparaciones entre serogrupos, serotipos, biotipos y ribotipos se podría establecer el sistema de ribotipificación como una nueva escala para la identificación y taxonomía en V. cholerae.
REFERENCIAS
1 . Sharma C, Ghosh A, Dalsgaard A, Forslund A, Ghosh R, Bhattacharya S, et al. Molecular evidence that a distinct Vibrio cholerae O1 biotype El Tor strain in Calcutta may have spread to the African continent. J Clin Microbiol 1998; 36(3): 843-4. [ Links ]
2. Lan R, Reeves R. Recombination between rDNA16S operons created most of the ribotype observed in the seventh pandemic clone of Vibrio cholerae. Microbiol 1998; 144:1213-21. [ Links ]
3. Popovic T, Bopp C, Olsvik O, Wachsmuth K. Epidemiologic application of a standardized ribotype scheme for Vibrio cholerae O1. J Clin Microbiol 1993; 31(9): 2474-82. [ Links ]
4. Instituto Nacional de Salud. Manual de PCR e Hibridación. Lima-Perú. 1998. [ Links ]
5. Southern E. Detection of specific sequences among DNA fragments separated by gel electrophoresis. J Mol Biol 1975; 98(3): 503-7. [ Links ]
6. Regnault B, Grimont F, Grimont P. Universal ribotyping method using a chemically labelled oligonucleotide probe mixture. Res Microbiol 1997; 148(8): 649-59. [ Links ]
7. Wilson K, Blitcington R, Greene R. Amplification of bacterial 16S Ribosomal DNA with polymerasa chain reaction. J Clin Microbiol 1990; 28(9): 1942-6. [ Links ]
8. Godfrey-Fausset PF, Stoker P. Aspects of tuberculosis in Africa. 3. Genetic fingerprinting for clues for the pathogenesis of tuberculosis. Trans R S Trop Med Hyg 1992; 86: 472-5. [ Links ]
9. Faruque SM, Abdul Alim AR, Roy SK, Khan F, Nair GB, Sack RB, et. al. Molecular analysis of rDNA 16S and cholera toxin genes carried by the new epidemia strain of toxigenic Vibrio cholerae O139 synonym Bengal. J Clin Microbiol 1994; 32(4): 1050-3. [ Links ]
10. Berche P, Poyart C, Abachin E, Lelievre H, Vandepitte J, Dodin A, et. al. The novel epidemia strain O139 is closely related to the pandemic strain O1 of Vibrio cholerae. J Infect Dis 1994; 170(3): 701-4 . [ Links ]
11. Dalsgaard A, Skov MN, Serichantalergs O, Echeverria P, Meza R, Taylor DN. Molecular evolution of Vibrio cholerae O1 strains isolated in Lima, Peru, from 1991 to 1995. J Clin Microbiol 1997; 35(5): 1151-6. [ Links ]
12. Janssen P, Coopman R, Huys G, Swings J, Bleeker M, Vos P, et. al. Evaluation of the DNA fingerprinting method AFLP as a new tool in bacterial taxonomy. Microbiology 1996; 142(Pt 7): 1881-93. [ Links ]
Correspondencia: José Huguet Tapia. Instituto Nacional de Salud. Calle Cápac Yupanqui 1400, Lima 11, Perú. Apartado Postal 471. Telf.:(0511) 4719920-Fax:(0511) 4710179.Email: enteropa@ins.sld.pe